Nom du projet : Online Morphogenesis
Type : Logiciel de visualisation 3D
Moteur : Unity
Equipe : 2
Rôle : Programmeur
Durée de production : 4 mois
Ce projet a été réalisé pendant mon stage de fin d'année 2016 de licence professionnelle au sein de l'équipe de recherche Virtual Plants à Montpellier. Il a consisté en la réalisation d'une application de visualisation en 3D d'embryon avec le moteur de jeu Unity. Durant son développement, j'ai utilisé un embryon, récemment reconstruit par les biologistes à partir d'images 3D + temps obtenus par microscopie, d'un organisme marin (Ascidie) jusqu'à la fin de la gastrulation (seconde phase de développement embryonnaire). J'ai ainsi pu créer une application permettant la manipulation de 192 pas de temps retraçant l'évolution des cellules de l'embryon.
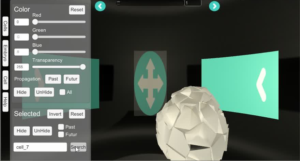
Chacun de ces pas de temps est présenté dans un document CSV qui contient toutes les informations de chaque pas de temps ainsi que des cellules qui y sont présentes, comme les cellules qu'elles vont former en se divisant, et donc leur moment d’apparition ou de mort, ainsi que des id propres afin de pouvoir les relier aux modèles 3D que j'ai eu à manipuler. Et afin de faciliter leur utilisation, j'ai créé une classe Cellule qui contiendrait ces informations ainsi que d'autres importantes pour la suite. De plus, cette classe était utilisée dans une liste qui contient les différentes cellules de chaque pas de temps.
L'application comporte différentes fonctions qui ont été classées en deux parties: les fonctions primaires qui regroupent les outils de première importance pour les biologistes et les fonctions utilitaires qui ajoutent un intérêt supplémentaire à l'application :
Fonctions Primaires :
Navigation spatiale
Navigation temporelle
Sélection
Modification des caractéristiques
Propagation des caractéristiques
Fonctions Utilitaires:
Coupe surfacique
Activation et désactivation des cellules
Recherche par nom
Détection des cellules voisines
Fenêtre d’aide
Cette interface doit être très intuitive pour être utilisée facilement par une communauté de biologistes non habitués aux logiciels complexes.